 단백질·분자 상호작용 유형 기반 3차원 생성형 AI 개념도./사진제공=KAIST
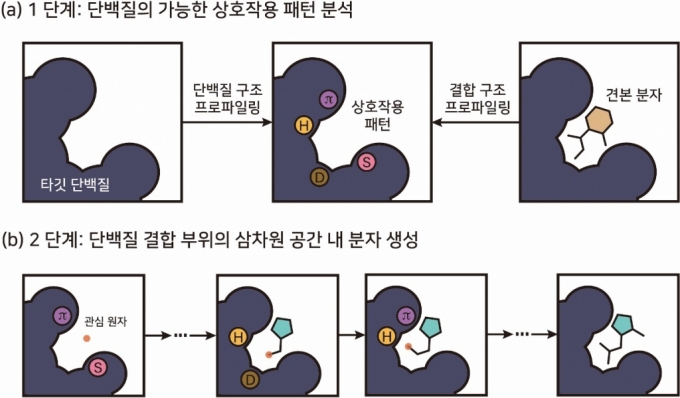
단백질·분자 상호작용 유형 기반 3차원 생성형 AI 개념도./사진제공=KAIST KAIST(카이스트)는 김우연 화학과 교수 연구팀이 단백질·분자 간 상호작용을 고려해 활성 데이터 없이도 표적 단백질에 적합한 '약물 설계 생성형 AI'를 개발했다고 18일 밝혔다.
신규 약물 발굴을 위해선 질병의 원인이 되는 표적 단백질에 결합하는 분자를 찾아내야 한다. 기존의 약물 설계 생성형 AI는 특정 단백질의 이미 알려진 활성 데이터를 학습에 활용하기 때문에, 기존 약물과 유사한 약물을 설계하려는 경향이 있다. 이는 신규성이 중요한 신약 개발 분야에서 약점으로 지적돼 왔고, 최초 표적 단백질의 경우 실험 데이터도 적어 기존의 생성형 AI 활용이 어려웠다.
 김우연 KAIST 화학과 교수./사진제공=KAIST
김우연 KAIST 화학과 교수./사진제공=KAIST 논문 1저자인 정원호 KAIST 화학과 박사과정 학생은 "사전 지식을 AI 모델에 사용하는 전략은 상대적으로 데이터가 적은 과학 분야에서 사용해 왔다"라며 "이번 연구에서 사용한 분자 간 상호작용 정보를 약물 분자뿐 아니라 다양한 생체 분자를 다루는 바이오 분야 문제에 유용하게 적용할 수 있다"라고 말했다.
한국연구재단의 지원을 받아 수행된 연구결과는 국제 학술지 '네이처 커뮤니케이션즈(Nature Communications)' 올해 3월 15호에 게재됐다.
